概要
レンチウイルスsgRNAライブラリを用いたCRISPRスクリーニングは、特定の表現型に必要とされる遺伝子を同定するための非常に効果的なアプローチであり、RNA-seqはそれらの表現型を生成する遺伝子の発現変化を検出する有効な手法です。また、RNA-seq と大規模なシングルセルの分子分析を可能にする液滴ベースのマイクロ流体プラットフォームを組み合わせて、CRISPRノックアウトスクリーニングにおける明確な発現プロファイルを評価し、特徴付けることができます。
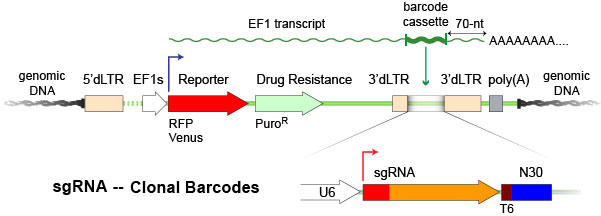
図1. バーコード標識 sgRNA
CloneTracker XP™ CRISPR バーコードライブラリはクローン細胞のトラッキングとシングルセル発現解析を容易にする独自の分子識別子(UMIまたはバーコード)を持つCRISPR遺伝子スクリーニング用のsgRNAを発現します。本ライブラリでは、バーコード化sgRNA発現カセットがピューロマイシン選択遺伝子の3 '非コード領域上にあり、この遺伝子が発現されるときにポリA +上に存在するように配置されています。そのため、sgRNAとバーコード配列はRNA シーケンスで検出することができます。シングルセル発現プロファイリングと組み合わせると、遺伝子発現の変化は、ライブラリを作製するために使用されるCRISPR構築物のタイプに依存して、遺伝子ノックアウト、ノックダウン、または活性化に直接関連付けることが可能です。
特徴
- mRNA-Seqで検出することができるバーコード標識sgRNA発現カセットライブラリ
- Perturb-SeqまたはCRISPR-Seqに適用可能
- ヒトおよびマウス遺伝子を標的とする2種類の相補的ライブラリ
CRISPR sgRNAライブラリに組み込まれた細胞特異的バーコードは、水滴の中に一個ずつ細胞をトラップするシングルセル遺伝子発現解析と組み合わせて、Perturb-SeqまたはCRISPR-Seq と呼ばれる手法で使用することができます。このアプローチにより、遺伝子発現の変化を確実に特定し、特定の標的遺伝子のノックアウトと結びつけることが可能になります。Cellecta社は現在、2つの相補的なCloneTracker XP CRISPRノックアウトライブラリを提供しており、1つは27種類のヒト抗がん遺伝子を標的にし、もう1つは27種類の対応するマウスホモログを標的としています。各遺伝子には機能ドメインを標的とするように設計された20種類のsgRNAが含まれます。






















 このページを印刷する
このページを印刷する















